- Description :
L’ensemble de données sur le paludisme contient un total de 27 558 images de cellules avec des instances égales de cellules parasitées et non infectées provenant des images de frottis sanguins minces de cellules segmentées.
Documentation supplémentaire : Explorer sur les articles avec le code
Page d'accueil : https://lhncbc.nlm.nih.gov/publication/pub9932
Code source :
tfds.datasets.malaria.BuilderVersions :
-
1.0.0(par défaut) : Aucune note de version.
-
Taille du téléchargement :
337.08 MiBTaille de l'ensemble de données :
317.62 MiBMise en cache automatique ( documentation ) : Non
Divisions :
| Diviser | Exemples |
|---|---|
'train' | 27 558 |
- Structure des fonctionnalités :
FeaturesDict({
'image': Image(shape=(None, None, 3), dtype=uint8),
'label': ClassLabel(shape=(), dtype=int64, num_classes=2),
})
- Documentation des fonctionnalités :
| Fonctionnalité | Classe | Forme | Type D | Description |
|---|---|---|---|---|
| FonctionnalitésDict | ||||
| image | Image | (Aucun, Aucun, 3) | uint8 | |
| étiquette | Étiquette de classe | int64 |
Clés supervisées (Voir doc
as_supervised) :('image', 'label')Figure ( tfds.show_examples ) :
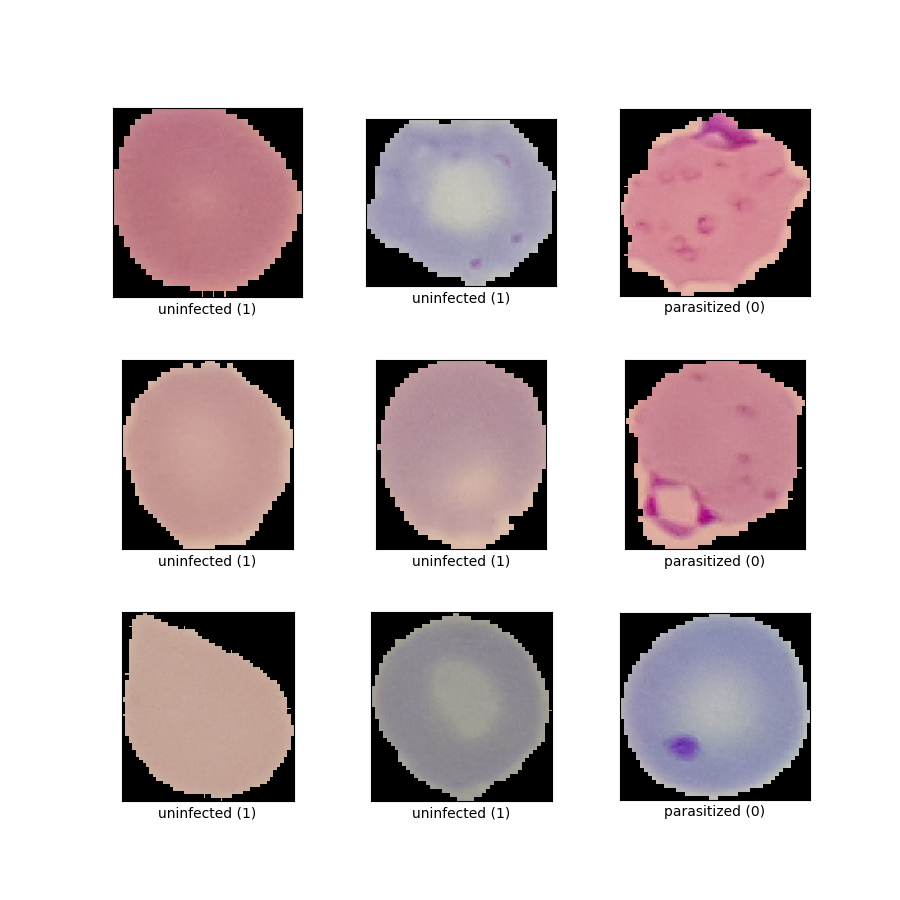
- Exemples ( tfds.as_dataframe ) :
- Citation :
@article{rajaraman2018pre,
title={Pre-trained convolutional neural networks as feature extractors toward
improved malaria parasite detection in thin blood smear images},
author={Rajaraman, Sivaramakrishnan and Antani, Sameer K and Poostchi, Mahdieh
and Silamut, Kamolrat and Hossain, Md A and Maude, Richard J and Jaeger,
Stefan and Thoma, George R},
journal={PeerJ},
volume={6},
pages={e4568},
year={2018},
publisher={PeerJ Inc.}
}

